
Votre histoire de cancer est unique. Vos soins devraient l'être aussi.
La compréhension de votre cancer commence ici.
De la biopsie tumorale à la biopsie liquide, OncoHelix propose une large gamme de panels de profilage génomique du cancer adaptés à vos besoins.
Votre traitement commence par une meilleure connaissance
Nos panels de profils génomiques complets
Aide au diagnostic du cancer
Aide à la classification des risques de cancer
Identifier des thérapies ciblées
Découvrez nos panels
-
Utilise le kit CGP Roche AVENIO Tumor tissue powered by FoundationOne Analysis Platform
Le test OncoHelix-1 offre les informations les plus approfondies sur la génomique du cancer. Le panel permet une exploration approfondie du génome tumoral, identifiant un large éventail d'altérations, notamment les SNV, les CNV, les Indels et les fusions. Le panel met en relation les patients avec les thérapies approuvées par la FDA, offre des informations sur les mécanismes de résistance et évalue des marqueurs tels que la charge mutationnelle tumorale et l'instabilité microsatellitaire, améliorant ainsi les décisions en matière d'immunothérapie.
-
Utilise le panel Illumina TST-170
Le test OncoHelix-2 (ADN+ARN) est un test avancé de profilage génomique. Ce panel CGP offre la flexibilité nécessaire pour détecter les altérations génétiques dans l'ADN et l'ARN d'une gamme de tumeurs solides. Il identifie les mutations exploitables, facilitant ainsi la personnalisation des traitements contre le cancer. Le panel aide à trouver les traitements ciblés adaptés à chaque patient et fournit des informations sur la résistance potentielle aux médicaments et le pronostic.
-
Utilise le panel Illumina TSO-500
Le panel CGP OncoHelix-3 offre la possibilité de détecter des altérations génétiques tant dans l'ADN que dans l'ARN d'un large éventail de tumeurs solides, conformément aux principales recommandations cliniques. Il couvre 523 gènes et inclut des cibles impliquées dans plus de 1 600 essais cliniques en cours. Ce test permet également d'obtenir des informations en immuno-oncologie grâce à l'évaluation intégrée de la charge mutationnelle tumorale (TMB) et de l'instabilité microsatellitaire (MSI). L'analyse du déficit en recombinaison homologue (HRD) est incluse, permettant la détection des variants BRCA1/2 et la détermination d'un score d'instabilité génomique (GIS).
-
Utilise le panel ctDNA de MSK-Access alimenté par la plateforme d'analyse SOPHiA DDM
OncoHelix-4 est un panel de biopsie liquide mini-invasive spécialement conçu pour les tumeurs solides. Utilisable comme méthode alternative ou complémentaire aux analyses tissulaires, il s'avère particulièrement utile lorsque le prélèvement d'échantillons tissulaires pose des difficultés considérables ou comporte des risques potentiels. Ce panel aide à adapter les traitements aux patients et fournit des informations sur la résistance potentielle aux médicaments et le pronostic.
-
Utilise le panel Myeloid Plus de SOPHiA GENETICS et la plateforme d'analyse SOPHiA DDM.
Ce panel offre un séquençage de nouvelle génération pour les tumeurs malignes myéloïdes, identifiant les altérations génétiques dans l'ADN et l'ARN à travers les gènes clés. Il permet un diagnostic précis, un pronostic et des décisions thérapeutiques pour les cancers myéloïdes. Ce panel permet de stratifier les risques et de suivre l'évolution de la maladie, fournissant ainsi des informations complètes pour une prise en charge personnalisée des patients.
-
Utilise le panneau Avitia Find It®.
OncoHelix - Follow It panel est un test à haute performance basé sur un panel d'amplicons, conçu pour le séquençage de nouvelle génération (NGS) afin de détecter les mutations génomiques cliniquement exploitables dans les biopsies de tumeurs solides. Il analyse 38 gènes associés au cancer, 26 exons et plus de 337 points chauds, en se concentrant sur les altérations génétiques clés qui indiquent la sensibilité et la résistance aux thérapies approuvées et expérimentales, ainsi que sur les biomarqueurs diagnostiques et pronostiques du cancer.
-
Utilise le panel Avitia Follow It® ctDNA.
Le panel OncoHelix - Follow It est un test de panel d'amplicons, conçu pour le séquençage de nouvelle génération (NGS) afin de détecter les mutations génomiques cliniquement exploitables dans l'ADN tumoral circulant exempt de cellules. Il analyse 38 gènes associés au cancer, 26 exons et plus de 337 points chauds, en se concentrant sur les altérations génétiques clés qui indiquent la sensibilité et la résistance aux thérapies approuvées et expérimentales, ainsi que sur les biomarqueurs diagnostiques et pronostiques du cancer.
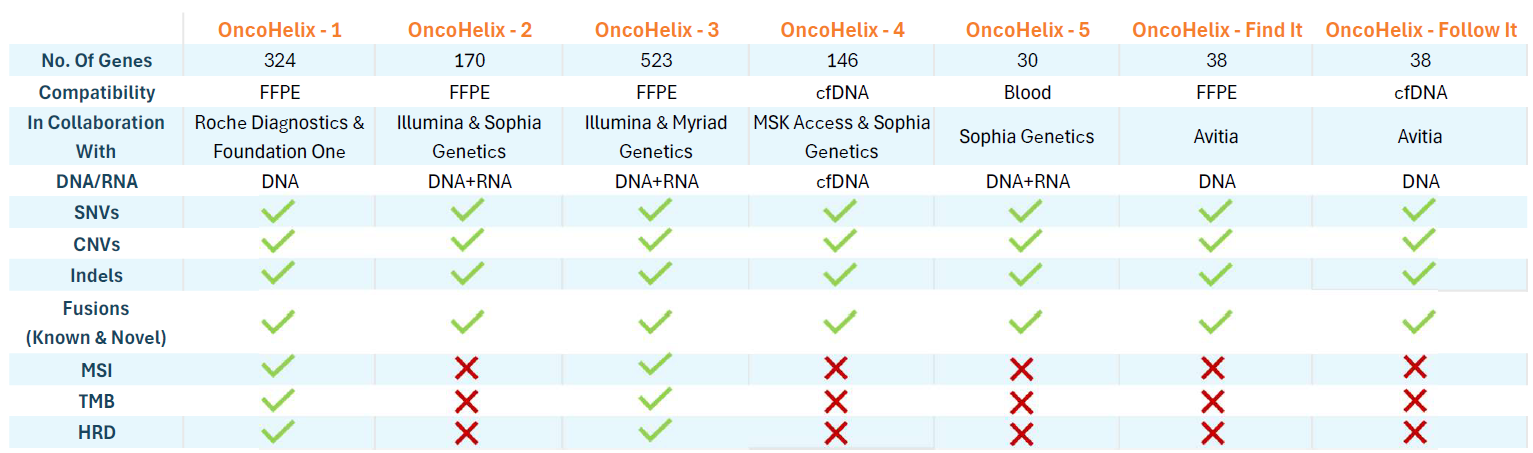
Comparez nos panneaux
Commander un test

Étape 1 Le médecin doit remplir la demande d'analyse génomique OncoHelix.
Les coordonnées du patient sont indiquées en haut de la demande sous la rubrique "Informations sur le patient".Les coordonnées du médecin sont indiquées dans la rubrique "Informations sur la commande".Le médecin indique le type de cancer du patient dans la rubrique "Diagnostic". Par exemple, Colorectal.Le médecin sélectionne le type de test de panel de gènes dans la rubrique "Demande de test". Une liste détaillée des gènes inclus dans chaque panel figure à la page 3 de la demande.

Étape 2 Envoyez la demande dûment remplie au laboratoire OncoHelix par fax au 403 210 8176.
Note : Le laboratoire et les tests NGS d'OncoHelix sont disponibles dans tous les sites au Canada, aux États-Unis et dans le monde entier. Les échantillons peuvent être expédiés au laboratoire OncoHelix pour être testés de n'importe où, il n'y a pas de limitation géographique pour effectuer un test NGS à partir de tissus ou de biopsies liquides.
Étape 3 OncoHelix vous contactera dans les 3 jours ouvrables.
Un conseiller client d'OncoHelix vous contactera par e-mail dans un délai de 3 jours ouvrables afin d'organiser la réalisation du test. Un lien de paiement sécurisé vous sera fourni pour vous faciliter la tâche. Toutes les principales cartes de crédit sont acceptées. Le conseiller client vous fournira également des instructions concernant les démarches supplémentaires à effectuer, le cas échéant.
Étape 4 Le rapport sur le profil génomique de la tumeur vous sera envoyé dans 4 semaines.
La réalisation du test CGP prend 4 semaines, depuis l'arrivée de l'échantillon préparé au laboratoire OncoHelix de Calgary (Alberta) jusqu'au résultat final examiné par notre équipe de pathologistes. Lorsque le test génomique est terminé et que le profil génomique est analysé, votre oncologue ou le médecin prescripteur recevra un rapport électronique. Le patient recevra également une copie du rapport. Formulaire de demande
Les résidents de l'Ontario, de la Colombie-Britannique et de la Saskatchewan devront remplir ce formulaire en plus de la demande ci-dessus. Panneau - Informations sur les gènes
-
Petites variantes (306) :
ABL1, ACVR1B, AKT1, AKT2, AKT3, ALK, ALOX12B, AMER1, APC, AR, ARAF, ARFRP1, ARID1A, ASXL1, ATM, ATR, ATRX, AURKA, AURKB, AXIN1, AXL, BAP1, BARD1, BCL2, BCL2L1, BCL2L2, BCL6, BCOR, BCORL1, BRAF, BRCA1, BRCA2, BRD4, BRIP1, BTG1, BTG2, BTK, C11orf30, CALR, CARD11, CASP8, CBFB, CBL, CCND1, CCND2, CCND3, CCNE1, CD22, CD274, CD70, CD79A, CD79B, CDC73, CDH1, CDK12, CDK4, CDK6, CDK8, CDKN1A, CDKN1B, CDKN2A, CDKN2B, CDKN2C, CEBPA, CHEK1, CHEK2, CIC, CREBBP, CRKL, CSF1R, CSF3R, CTCF, CTNNA1, CTNNB1, CUL3, CUL4A, CXCR4, CYP17A1, DAXX, DDR1, DDR2, DIS3, DNMT3A, DOT1L, EED, EGFR, EP300, EPHA3, EPHB1, EPHB4, ERBB2, ERBB3, ERBB4, ERCC4, ERG, ERRFI1, ESR1, EZH2, FAM46C, FANCA, FANCC, FANCG, FANCL, FAS, FBXW7, FGF10, FGF12, FGF14, FGF19, FGF23, FGF3, FGF4, FGF6, FGFR1, FGFR2, FGFR3, FGFR4, FH, FLCN, FLT3, FOXL2, FUBP1, GABRA6, GATA3, GATA4, GATA6, GID4 (C17orf39), GNA11, GNA13, GNAQ, GNAS, GRM3, GSK3B, H3F3A, HDAC1, HGF, HNF1A, HRAS, HSD3B1, ID3, IDH1, IDH2, IGF1R, IKBKE, IKZF1, INPP4B, IRF2, IRF4, IRS2, JAK1, JAK2, JAK3, JUN, KDM5A, KDM5C, KDM6A, KDR, KEAP1, KEL, KIT, KLHL6, KMT2A (MLL), KMT2D (MLL2), KRAS, LTK, LYN, MAF, MAP2K1, MAP2K2, MAP2K4, MAP3K1, MAP3K13, MAPK1, MCL1, MDM2, MDM4, MED12, MEF2B, MEN1, MERTK, MET, MITF, MKNK1, MLH1, MPL, MRE11A, MSH2, MSH3, MSH6, MST1R, MTAP, MTOP, MUTYH, MYC, MYCL, MYCN, MYD88, NBN, NF1, NF2, NFE2L2, NFKBIA, NKX2-1, NOTCH1, NOTCH2, NOTCH3, NPM1, NRAS, NT5C2, NTRK1, NTRK2, NTRK3, P2RY8, PALB2, PARK2, PARP1, PARP2, PARP3, PAX5, PBRM1, PDCD1, PDCD1LG2, PDGFRA, PDGFRB, PDK1, PIK3C3B, PIK3C3G, PIK3CA, PIK3CB, PIK3R1, PIM1, PMS2, POLD1, POLE, PPARG, PPP2R1A, PPP2R2A, PRDM1, PRKAR1A, PRKCI, PTCH1, PTEN, PTPN11, PTPRO, QKI, RAC1, RAD21, RAD51, RAD51B, RAD51C, RAD51D, RAD52, RAD54L, RAF1, RARA, RB1, RBM10, REL, RET, RICTOR, RNF43, ROS1, RPTOR, SDHA, SDHB, SDHC, SDHD, SETD2, SF3B1, SGK1, SMAD2, SMAD4, SMARCA4, SMARCB1, SMO, SNCAIP, SOCS1, SOX2, SOX9, SPEN, SPOP, SRC, STAG2, STAT3, STK11, SYK, TBX3, TEK, TET2, TIPARP, TNFAIP3, TNFRSF14, TP53, TSC1, TSC2, TYRO3, U2AF1, VEGFA, VHL, WHSC1, WHSC1L1, WT1, XPO1, XRCC2, ZNF217, ZNF703
Gènes cibles des fusions d'ADN (36):
ALK, BCL2, BCR, BRAF, BRCA1, BRCA2, CD74, EGFR, ETV4, ETV5, ETV6, EWSR1, EZR, FGFR1, FGFR2, FGFR3, KIT, KMT2A (MLL), MSH2, MYB, MYC, NOTCH2, NTRK1, NTRK2, NUTM1, PDGFRA, RAF1, RARA, RET, ROS1, RSPO2, SDC4, SLC34A2, TERC, TERT, TMPRSS2
-
Compatibilité des échantillons : ADN et ARN génomiques extraits de tissus frais congelés et FFPE
LES GÈNES DE L'ADN :
Petits variants et indels (148) : AKT1, AKT2, AKT3, ALK, APC, AR, ARID1A, ATM, ATR, BAP1, BARD1, BCL2, BCL6, BRAF, BRCA1, BRCA2, BRIP1, BTK, CARD11, CCND1, CCND2, CCNE1, CD79A, CD79B, CDH1, CDK12, CDK4, CDK6, CDKN2A, CEBPA, CHEK1, CHEK2, CREBBP, CSF1R, CTNNB1, DDR2, DNMT3A, EGFR, EP300, ERBB2, ERBB3, ERBB4, ERCC1, ERG, ESR1, EZH2, FAM175A, FANCI, FANCL, FBXW7, FGF1, FGF10, FGF2, FGF23, FGF3, FGF4, FGF5, FGF7, FGF9, FGFR1, FGFR2, FGFR3, FGFR4, FLT1, FLT3, FOXL2, GNA11, GNAQ, GNAS, HNF1A, HRAS, IDH1, IDH2, INPP4B, JAK2, JAK3, KDR, KIT, KRAS, MAP2K1, MAP2K2, MCL1, MDM2, MDM4, MET, MLH1, MLLT3, MPL, MRE11A, MSH2, MSH3, MSH6, MTOR, MUTYH, MYC, MYCN, MYD88, NBN, NF1, NOTCH1, NOTCH2, NOTCH3, NPM1, NRAS, NRG1, PALB2, PDGFRA, PDGFRB, PIK3CA, PIK3CB, PIK3CD, PIK3CG, PIK3R1, PMS2, PTCH1, PTEN, PTPN11, RAD51B, RAD51C, RAD54L, RB1, RET, RICTOR, ROS1, SLX4, SMAD4, SMARCB1, SMO, STK11, TET2, TP53, TSC1, TSC2
gènes cibles de l'amplification de l'ADN (59) : AKT2, ALK, AR, ATM, BRAF, BRCA1, BRCA2, CCND1, CCND3, CCNE1, CDK4, CDK6, CHEK1, CHEK2, EGFR, ERBB2, ERBB3, ERCC1, ERCC2, ESR1, FGF1, FGF10, FGF14, FGF19, FGF2, FGF23, FGF3, FGF4, FGF5, FGF6, FGF7, FGF8, FGF9, FGFR1, FGFR2, FGFR3, FGFR4, JAK2, KIT, KRAS, LAMP1, MDM2, MDM4, MET, MYC, MYCL1, MYCN, NRAS, NRG1, PDGFRA, PDGFRB, PIK3CA, PIK3CB, PTEN, RAF1, RET, RICTOR, RPS6KB1, TFRCGENES ARN :
Gènes cibles de la fusion ARN (55) : ABL1, AKT3, ALK, AR, AXL, BCL2, BRAF, BRCA1, BRCA2, CDK4, CSF1R, EGFR, EML4, ERBB2, ERG, ESR1, ETS1, ETV1, ETV4, ETV5, EWSR1, FGFR1, FGFR2, FGFR3, FGFR4, FLI1, FLT1, FLT3, JAK2, KDR, KIF5B, KIT, KMT2A (MLL), MET, MLLT3, MSH2, MYC, NOTCH1, NOTCH2, NOTCH3, NRG1, NTRK1, NTRK2, NTRK3, PAX3, PAX7, PDGFRA, PDGFRB, PIK3CA, PPARG, RAF1, RET, ROS1, RPS6KB1, TMPRSS2
-
Compatibilité des échantillons : ADN et ARN génomiques extraits de tissus frais congelés et FFPE
LES GÈNES DE L'ADN :
Variants mineurs et indels, gènes cibles d'amplification : ABL1, ABL2, ACVR1, ACVR1B, AKT1, AKT2, AKT3, ALK, ALOX12B, ANKRD11, ANKRD26, APC, AR, ARAF, ARFRP1, ARID1A, ARID1B, ARID2, ARID5B, ASXL1, ASXL2, ATM, ATR, ATRX, AURKA, AURKB, AXIN1, AXIN2, AXL, B2M, BAP1, BARD1, BBC3, BCL10, BCL2, BCL2L1, BCL2L11, BCL2L2, BCL6, BCOR, BCORL1, BCR, BIRC3, BLM, BMPR1A, BRAF, BRCA1, BRCA2, BRD4, BRIP1, BTG1, BTK, C11orf30, CALR, CARD11, CASP8, CBFB, CBL, CCND1, CCND2, CCND3, CCNE1, CD274, CD276, CD74, CD79A, CD79B, CDC73, CDH1, CDK12, CDK4, CDK6, CDK8, CDKN1A, CDKN1B, CDKN2A, CDKN2B, CDKN2C, CEBPA, CENPA, CHD2, CHD4, CHEK1, CHEK2, CIC, CREBBP, CRKL, CRLF2, CSF1R, CSF3R, CSNK1A1, CTCF, CTLA4, CTNNA1, CTNNB1, CUL3, CUX1, CXCR4, CYLD, DAXX, DCUN1D1, DDR2, DDX41, DHX15, DICER1, DIS3, DNAJB1, DNMT1, DNMT3A, DNMT3B, DOT1L, E2F3, EED, EGFL7, EGFR, EIF1AX, EIF4A2, EIF4E, EML4, EP300, EPCAM, EPHA3, EPHA5, EPHA7, EPHB1, ERBB2, ERBB3, ERBB4, ERCC1, ERCC2, ERCC3, ERCC4, ERCC5, ERG, ERRFI1, ESR1, ETS1, ETV1, ETV4, ETV5, ETV6, EWSR1, EZH2, FAM123B, FAM175A, FAM46C, FANCA, FANCC, FANCD2, FANCE, FANCF, FANCG, FANCI, FANCL, FAS, FAT1, FBXW7, FGF1, FGF10, FGF14, FGF19, FGF2, FGF23, FGF3, FGF4, FGF5, FGF6, FGF7, FGF8, FGF9, FGFR1, FGFR2, FGFR3, FGFR4, FH, FLCN, FLI1, FLT1, FLT3, FLT4, FOXA1, FOXL2, FOXO1, FOXP1, FRS2, FUBP1, FYN, GABRA6, GATA1, GATA2, GATA3, GATA4, GATA6, GEN1, GID4, GLI1, GNA11, GNA13, GNAQ, GNAS, GPR124, GPS2, GREM1, GRIN2A, GRM3, GSK3B, H3F3A, H3F3B, H3F3C, HGF, HIST1H1C, HIST1H2BD, HIST1H3A, HIST1H3B, HIST1H3C, HIST1H3D, HIST1H3E, HIST1H3F, HIST1H3G, HIST1H3H, HIST1H3I, HIST1H3J, HIST2H3D, HIST3H3, HNF1A, HNRNPK, HOXB13, HRAS, HSD3B1, HSP90AA1, ICOSLG, ID3, IDH1, IDH2, IFNGR1, IGF1, IGF1R, IGF2, IKBKE, IKZF1, IL10, IL7R, INHA, INHBA, INPP4A, INPP4B, INSR, IRF2, IRF4, IRS1, IRS2, JAK1, JAK2, JAK3, JUN, KAT6A, KDM5A, KDM5C, KDM6A, KDR, KEAP1, KEL, KIF5B, KIT, KLF4, KLHL6, KRAS, LAMP1, LATS1, LATS2, LMO1, LRP1B, LYN, LZTR1, MAGI2, MALT1, MAP2K1, MAP2K2, MAP2K4, MAP3K1, MAP3K13, MAP3K14, MAP3K4, MAPK1, MAPK3, MAX, MCL1, MDC1, MDM2, MDM4, MED12, MEF2B, MEN1, MET, MGA, MITF, MLH1, MLL, MLLT3, MPL, MRE11A, MSH2, MSH3, MSH6, MST1, MST1R, MTOR, MUTYH, MYB, MYC, MYCL1, MYCN, MYD88, MYOD1, NAB2, NBN, NCOA3, NCOR1, NEGR1, NF1, NF2, NFE2L2, NFKBIA, NKX2-1, NKX3-1, NOTCH1, NOTCH2, NOTCH3, NOTCH4, NPM1, NRAS, NRG1, NSD1, NTRK1, NTRK2, NTRK3, NUP93, NUTM1, PAK1, PAK3, PAK7, PALB2, PARK2, PARP1, PAX3, PAX5, PAX7, PAX8, PBRM1, PDCD1, PDCD1LG2, PDGFRA, PDGFRB, PDK1, PDPK1, PGR, PHF6, PHOX2B, PIK3C2B, PIK3C2G, PIK3C3, PIK3CA, PIK3CB, PIK3CD, PIK3CG, PIK3R1, PIK3R2, PIK3R3, PIM1, PLCG2, PLK2, PMAIP1, PMS1, PMS2, PNRC1, POLD1, POLE, PPARG, PPM1D, PPP2R1A, PPP2R2A, PPP6C, PRDM1, PREX2, PRKAR1A, PRKCI, PRKDC, PRSS8, PTCH1, PTEN, PTPN11, PTPRD, PTPRS, PTPRT, QKI, RAB35, RAC1, RAD21, RAD50, RAD51, RAD51B, RAD51C, RAD51D, RAD52, RAD54L, RAF1, RANBP2, RARA, RASA1, RB1, RBM10, RECQL4, REL, RET, RFWD2, RHEB, RHOA, RICTOR, RIT1, RNF43, ROS1, RPS6KA4, RPS6KB1, RPS6KB2, RPTOR, RUNX1, RUNX1T1, RYBP, SDHA, SDHAF2, SDHB, SDHC, SDHD, SETBP1, SETD2, SF3B1, SH2B3, SH2D1A, SHQ1, SLIT2, SLX4, SMAD2, SMAD3, SMAD4, SMARCA4, SMARCB1, SMARCD1, SMC1A, SMC3, SMO, SNCAIP, SOCS1, SOX10, SOX17, SOX2, SOX9, SPEN, SPOP, SPTA1, SRC, SRSF2, STAG1, STAG2, STAT3, STAT4, STAT5A, STAT5B, STK11, STK40, SUFU, SUZ12, SYK, TAF1, TBX3, TCEB1, TCF3, TCF7L2, TERC, TERTa, TET1, TET2, TFE3, TFRC, TGFBR1, TGFBR2, TMEM127, TMPRSS2, TNFAIP3, TNFRSF14, TOP1, TOP2A, TP53, TP63, TRAF2, TRAF7, TSC1, TSC2, TSHR, U2AF1, VEGFA, VHL, VTCN1, WISP3, WT1, XIAP, XPO1, XRCC2, YAP1, YES1, ZBTB2, ZBTB7A, ZFHX3, ZNF217, ZNF703, ZRSR2
GENES ARN :Gènes cibles de fusion ARN (55) : ABL1, AKT3, ALK, AR, AXL, BCL2, BRAF, BRCA1, BRCA2, CDK4, CSF1R, EGFR, EML4, ERBB2, ERG, ESR1, ETS1, ETV1, ETV4, ETV5, EWSR1, FGFR1, FGFR2, FGFR3, FGFR4, FLI1, FLT1, FLT3, JAK2, KDR, KIF5B, KIT, MET, MLL, MLLT3, MSH2, MYC, NOTCH1, NOTCH2, NOTCH3, NRG1, NTRK1, NTRK2, NTRK3, PAX3, PAX7, PDGFRA, PDGFRB, PIK3CA, PPARG, RAF1, RET, ROS1, RPS6KB1, TMPRSS2
-
Compatibilité des échantillons : ADNct et ADN génomique extraits respectivement d'échantillons de plasma et de sang total.
Petits variants et indels (144) : APC, AR, ARID1A, ASXL1, ATM, BAP1, BRCA1, BRCA2, CDK12, CDK4, CDKN2A, CHEK2, DNMT3A, ERCC2, FBXW7, FOXL2, GATA3, HIST1H3B, KDM6A, KEAP1, KRAS, MLH1, MSH2, MSH6, NFI, PALB2, PMS2, PPM1D, PTCH1, PTEN, RB1, SMAD4, STK11, TET2, TP53, TSC1, TSC2, VHL, ALK, BRAF, EGFR, FGFR2, FGFR3, MET, NTRK1, RET, ROS1, ETV6, AKT1, ARAF, ARID2, B2M, BCL2, BCOR, CARD11, CBFB, CBL, CCND1, CD79B, CDH1, CIC, CREBBP, CTCF, CTNNB1, DICER1, DIS3, EIF1AX, EP300, ERBB2, ERBB3, ESR1, EZH2, FGFR1, FGFR4, FLT3, FOXA1, FOXO1, FOXP1, FUBP1, GNA11, GNAQ, GNAS, H3F3A, HRAS, IDH1, IDH2, IKZF1, INPPL1, JAK1, JAK2, KIT, KNSTRN, MAP2K1, MAP2K2, MAPK1, MAX, MED12, MSH3, MTOR, MYC, MYCN, MYD88, MYOD1, NFE2L2, NOTCH1, NPM1, NRAS, NTRK2, NTKR3, NUP93, PAK5, PDGFRA, PHF6, PIK3CA, PIK3CB, PIK3R1, PIK3R2, PIM1, POLE, POT1, PPP2R1A, PPP6C, PRKCI, PTPN11, RAC1, RAD54L, RAF1, RHOA, RIT1, RRAS2, RXRA, SETD2, SF3B1, SOS1, SPOP, SRSF2, STAT3, STK19, TCF7L2, TGFBR1, TGFBR2, TP63, U2AF1, XPO1
Gènes cibles de l'amplification de l'ADN (38) : APC, AR, ARID1A, ASXL1, ATM, BAP1, BRCA1, BRCA2, CDK12, CDK4, CDKN2A, CHEK2, DNMT3A, ERCC2, FBXW7, FOXL2, GATA3, HIST1H3B, KDM6A, KEAP1, KRAS, MLH1, MSH2, MSH6, NF1, PALB2, PMS2, PPM1D, PTCH1, PTEN, RB1, SMAD4, STK11, TET2, TP53, TSC1, TSC2, VHL
Fusions d'ADN (10) : ALK, BRAF, EGFR, FGFR2, FGFR3, MET, NTRK1, RET, ROS1, ETV6
-
Fusions d'ARN ciblées
ATF7IP-JAK2 ; BCR-ABL1 ; BCR-FGFR1 ; BCR-JAK2 ; BCR-PDGFRA ; BMP2K-ZNF384 ; CBFA2T3-GLIS2 ; CBFB-MYH11 ; CCDC6PDGFRB ; CHIC2-ETV6 ; CNTRL-FGFR1 ; CREBBP-ZNF384 ; CUX1-FGFR1 ; DEK-NUP214 ; EBF1JAK2 ; EBF1-PDGFRB ; EML1-ABL1 ; EP300-ZNF384 ; ETV6-ABL1 ; ETV6-ARNT ; ETV6-JAK2 ; ETV6-NTRK3 ; ETV6-NTRK3 ; ETV6-PDGFRB ; ETV6-RU NX1 ; ETV6RUNX1 ; FGFR1OP-FGFR1 ; FIP1L1-PDGFRA ; FOXP1-ABL1 ; INPP5D-ABL1 ; KAT6A-CREBBP ; KMT2AAFDN ; KMT2A-AFF1 ; KMT2A-AFF3 ; KMT2A-AFF4 ; KMT2A-ARHGAP26 ; KMT2AARHGEF12 ; KMT2AARHGEF17 ; KMT2A-C2CD3 ; KMT2A-CBL ; KMT2A-CIP2A ; KMT2A-CREBBP ; KMT2A-DCPS ; KMT2A-ELL ; KMT2A-EPS15 ; KMT2A-FOXO3 ; KMT2AKMT2A ; KMT2A-KNL1 ; KMT2A-MAML2 ; KMT2AMAPRE1 ; KMT2A-MLLT1 ; KMT2AMLLT10 ; KMT2A-MLLT11 ; KMT2A-MLLT3 ; KMT2A-MLLT6 ; KMT2A-NRIP3 ; KMT2A-RARA ; KMT2A-SEP5 ; KMT2A-SEPT6 ; KMT2A-SEPT9 ; KMT2A-SEPT9 ; KMT2ATET1 ; MEF2D-CSF1R ; MN1-ETV6 ; MNX1-ETV6 ; MYB-GATA1 ; NCOR1-LYN ; NDE1-PDGFRB ; NPM1-MLF1 ; NPM1RARA ; NUP214-ABL1 ; NUP98-DDX10 ; NUP98-HOXA9 ; NUP98-KDM5A ; NUP98-NSD1 ; NUP98-RAP1GDS1 ; NUP98-TOP1 ; OFD1-JAK2 ; P2RY8-CRLF2 ; PAG1-ABL2 ; PAX5-ETV6 ; PAX5-JAK2 ; PAX5-ETV6 ; PAX5-JAK2 ; PCM1-JAK2 ; PDE4DIP-PDGFRB ; PICALM-MLLT10 ; PML-RARA ; RANBP2-ABL1 ; RBM15-MKL1 ; RCSD1-ABL1 ; RUNX1-RUNX1T1 ; SET-NUP214 ; SFPQ-ABL1 ; SNX2-ABL1 ; SPAG9-JAK2 ; SPTBN1FLT3 ; SPTBN1-PDGFRB ; SSBP2-CSF1R ; SSBP2-JAK2 ; STAT5B-RARA ; STIL-TAL1 ; STRN-PDGFRA ; STRN3-JAK2 ; TAF15-ZNF384 ; TCF3-HLF ; TCF3-PBX1 ; TERF2JAK2 ; TPM3-PDGFRB ; TPR-FGFR1 ; TRIM24-FGFR1 ; ZBTB16-ABL1 ; ZBTB16-RARA ; ZC3HAV1ABL2 ; ZEB2-PDGFRB ; ZMIZ1-ABL1 ; ZMYM2-FGFR1
Cibles ADN (Exons) Détails de la couverture
ABL1 (4-9) ; ASXL1 (10,12,13) ; BRAF (15) ; CALR (9) ; CBL (8,9) ; CEBPA (complet) ; CSF3R (complet) ; DNMT3A (complet) ; ETV6 (complet) ; EZH2 (complet) ; FLT3 (13-15,20) ; HRAS (2,3) ; IDH1 (4) ; IDH2 (4) ; JAK2 (complet) ; KIT (2,8-11,13,17,18) ; KRAS (2,3) ; MPL (10) ; NPM1 (10,11) ; NRAS (2,3) ; PTPN11 (3,7-13) ; RUNX1 (complète) ; SETBP1 (4) ; SF3B1 (10- 16) ; SRSF2 (1) ; TET2 (complète) ; TP53 (complète) ; U2AF1 (2,6) ; WT1 (6-10) ; ZRSR2 (complète)
-
AKT1 (E17), ALK (T1151, L1152, C1156, F1174, L1196, L1198, G1202, D1203, S1206, G1269, R1275, Y1278), AR (L702, V716, S741, W742, Q784, H875, F877, T878, M896), BRAF (Q201, G464, G466, F468, G469, Y472, D594, F595, G596, L597, V600, K601, partie de l'Exon15 (V600-M620), G606), CTNNB1 (D32, S33, G34, I35, H36, S37, T41, S45), CCNE1 (amplification), DDR2 (L239, I638, S768), DICER1 (D1705-D1709, G1809, D1810-E1813), EGFR (R108, A289, S492, P596, G598, Exon18 (E709, L718, G719), Exon19 (L747, A750, K754), Exon20 (S768, T790, L792, G796, C797, L798), Exon21 (L833, L838, L858, L861), Amplification), ERBB2 (G309, S310, K753, L755, I767, D769, Exon20 (V773, G776, V777), Amplification), ESFR1 (K303, E380, S463, V534, P535, L536, Y537, D538), FGFR1 (N546, K656, Amplification), FGFR2 (S252, P253, W290, A315, S372, Y375, C382, N549, K659, E731, E777, amplification), FGFR3 (R248, S249, G370, S371, Y373, G380, A391, K650), FOXL2 (C134), GNA11 (Q209), GNAQ (Q209), GNAS (R201), HRAS (G12, G13, Q61), IDH1 (R132), IDH2 (R140, R172), KIT (S476, Y553, W557, V559, V560, L576, K642, V654, T670, D816, D820, N822, Y823, A829, Exon9, Exon11, Exon13, Amplification), KRAS (K5, A11, G12, G13, L19, Q22, A59, G60, Q61, K117, A146, Amplification), MAP2K1 (F53, Q56, K57, K59, V60, D67, I103, I111, C121, N122, P124, P387), MAP2K2 (F57, Q60, K61, L119, H123, G132), MET (T1010, V1110, H1112, V1206, L1213, D1246, Y1248, Y1253, Exon13, Exon14 , Exon 14 skipping regions, Exon18, Amplification), NRAS (G12, G13, A59, G60, Q61, K117, A146), NTRK1 (F589, G595, G667), NTRK3 (G623, G696), PDGFRA (R560-E571, P577, N659, L839-Y849, D842), PIK3CA(R88, C90, R93, P104, G106, N107, R108, K111, R115, N345, R357, G364, E365, Exon6 [début à P377], C420, E453, P539, E542, E545, Q546, D549, E970, E978, M1043, N1044, A1046, H1047, G1049 Amplification), POLE (Exons 9-14 (P286R, M295R, S297F, F367S, D368Y, V411L, L424I, M444K, A456P, S459F)), PTCH1 (W844, G1093), PTEN(A126, G129, R130, R173, R233, K254-K267), RET (G533, K603, C609, C611, C618, C620, C630, D631, C634, G691, E768, L790, Y791, V804, Y806, A883, R886, S904, M918, A919, Exon10, Exon 13, Exon15), ROS1 (S1986, L2026, G2032), STK11 (Q37, P281), TP53 (Exons 2-11), MSI (21 amplicons)
-
AKT1 (E17), ALK (T1151, L1152, C1156, F1174, L1196, L1198, G1202, D1203, S1206, G1269, R1275, Y1278), AR (L702, V716, S741, W742, Q784, H875, F877, T878, M896), BRAF (Q201, G464, G466, F468, G469, Y472, D594, F595, G596, L597, V600, K601, partie de l'Exon15 (V600-M620), G606), CTNNB1 (D32, S33, G34, I35, H36, S37, T41, S45), CCNE1 (amplification), DDR2 (L239, I638, S768), DICER1 (D1705-D1709, G1809, D1810-E1813), EGFR (R108, A289, S492, P596, G598, Exon18 (E709, L718, G719), Exon19 (L747, A750, K754), Exon20 (S768, T790, L792, G796, C797, L798), Exon21 (L833, L838, L858, L861), Amplification), ERBB2 (G309, S310, K753, L755, I767, D769, Exon20 (V773, G776, V777), Amplification), ESFR1 (K303, E380, S463, V534, P535, L536, Y537, D538), FGFR1 (N546, K656, Amplification), FGFR2 (S252, P253, W290, A315, S372, Y375, C382, N549, K659, E731, E777, amplification), FGFR3 (R248, S249, G370, S371, Y373, G380, A391, K650), FOXL2 (C134), GNA11 (Q209), GNAQ (Q209), GNAS (R201), HRAS (G12, G13, Q61), IDH1 (R132), IDH2 (R140, R172), KIT (S476, Y553, W557, V559, V560, L576, K642, V654, T670, D816, D820, N822, Y823, A829, Exon9, Exon11, Exon13, Amplification), KRAS (K5, A11, G12, G13, L19, Q22, A59, G60, Q61, K117, A146, Amplification), MAP2K1 (F53, Q56, K57, K59, V60, D67, I103, I111, C121, N122, P124, P387), MAP2K2 (F57, Q60, K61, L119, H123, G132), MET (T1010, V1110, H1112, V1206, L1213, D1246, Y1248, Y1253, Exon13, Exon14 , Exon 14 skipping regions, Exon18, Amplification), NRAS (G12, G13, A59, G60, Q61, K117, A146), NTRK1 (F589, G595, G667), NTRK3 (G623, G696), PDGFRA (R560-E571, P577, N659, L839-Y849, D842), PIK3CA(R88, C90, R93, P104, G106, N107, R108, K111, R115, N345, R357, G364, E365, Exon6 [début à P377], C420, E453, P539, E542, E545, Q546, D549, E970, E978, M1043, N1044, A1046, H1047, G1049 Amplification), POLE (Exons 9-14 (P286R, M295R, S297F, F367S, D368Y, V411L, L424I, M444K, A456P, S459F)), PTCH1 (W844, G1093), PTEN(A126, G129, R130, R173, R233, K254-K267), RET (G533, K603, C609, C611, C618, C620, C630, D631, C634, G691, E768, L790, Y791, V804, Y806, A883, R886, S904, M918, A919, Exon10, Exon 13, Exon15), ROS1 (S1986, L2026, G2032), STK11 (Q37, P281), TP53 (Exons 2-11), MSI (21 amplicons)
